Förderjahr 2020 / Project Call #15 / ProjektID: 5171 / Projekt: OpenBioLink
Nachdem wir eine geeignete Software Architekture für den Explorer gefunden haben (siehe letzter Blog Post), möchten wir mit diesem Beitrag eine erste Alpha Version vorstellen (abrufbar unter http://explore.ai-strategies.org). Das öffentliche Code-Repository des Explorers kann man unter https://github.com/OpenBioLink/Explorer einsehen. Wie schon im vorigen Blog Post erwähnt wurde das Frontend der Webapplikation mittels des Javascript-Framework ReactJS implementiert, während das Backend auf NodeJS und einer Graphendatenbank mit SPARQL REST API (Blazegraph) basiert.
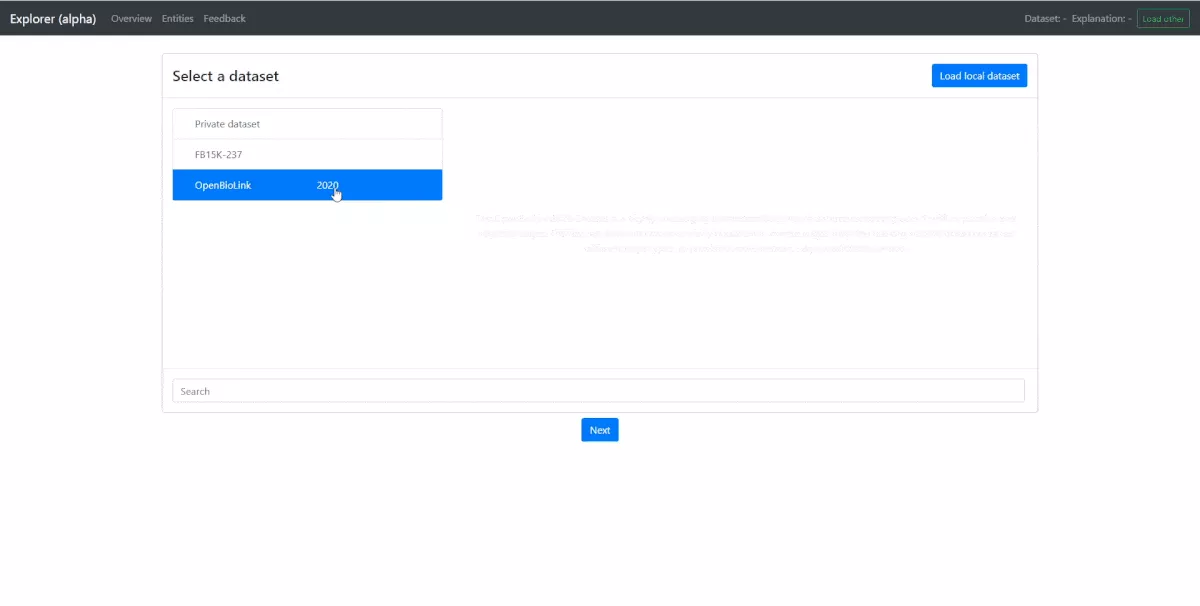
Nachdem der Benutzer einen Datensatz ausgewählt hat, kann er alle verknüpften Explanation-Files einsehen (Explanation-Files können sich hinsichtlich Regeln, Aggregationsmethoden, Hyperparameter etc. unterscheiden). Wählt der Benutzer ein Explanation-File lädt die Applikation eine Übersicht aller Entitäten des Test-Sets des Datensatzes.
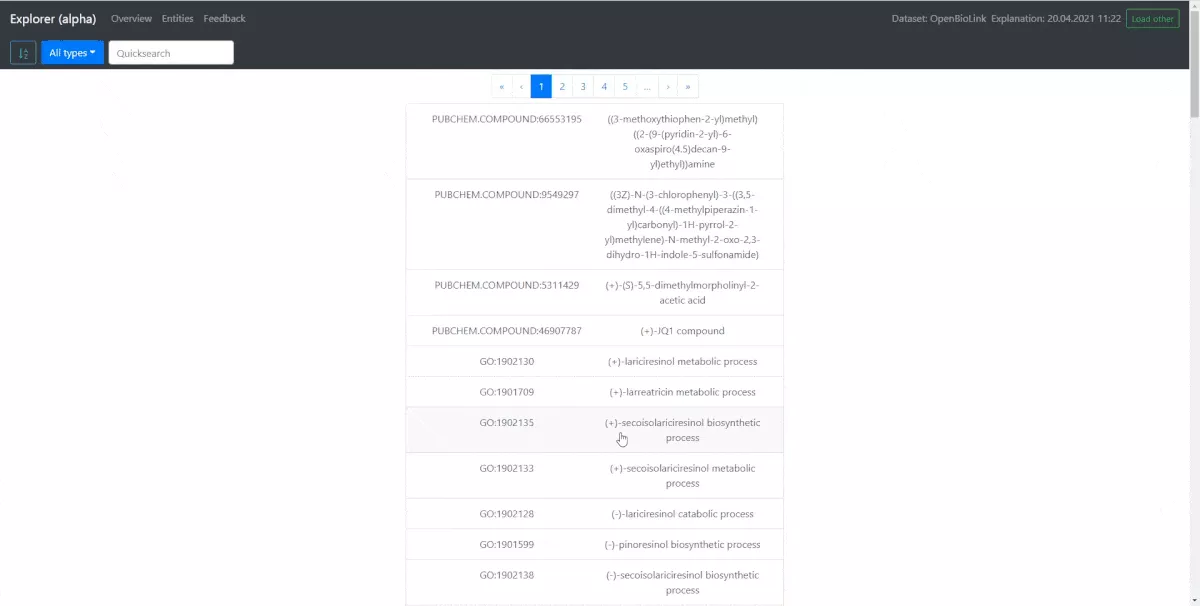
Alle Entitäten des Test-Sets und deren Labels werden dem Benutzer in Form einer Liste dargestellt. Diese Entitäten können sortiert, nach Typen gefiltert und durchsucht werden. Wählt der Benutzer eine Entität aus der Liste, öffnet sich eine Detailansicht.
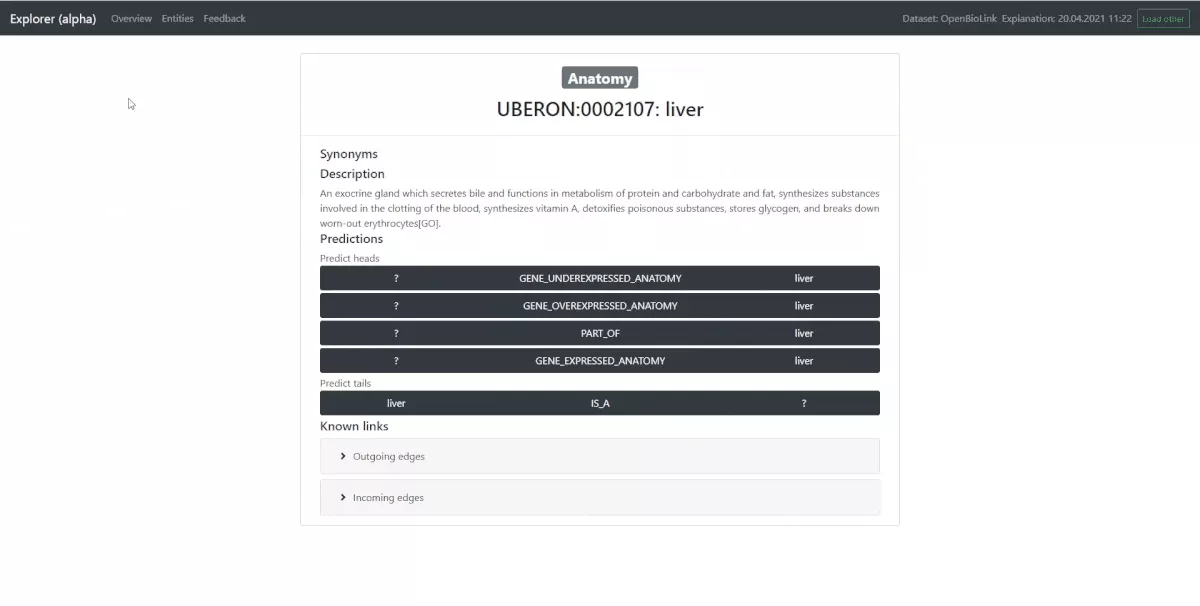
In der Detailansicht kann der Benutzer nähere Informationen über eine Entität einsehen. Diese beinhalten neben Label, Code, Beschreibung und Synonyme auch bekannte Verknüpfungen im Datensatz. Dabei wird zwischen ausgehenden (Entität ist Head, siehe voriger Blog Post) und eingehenden Kanten (Entität ist Tail) unterschieden. Weiters kann der Benutzer einen sogenannten “Prediction Task” auswählen. Ein “Prediction Task” ist die Vorhersage von Entitäten die mit dieser Entität verbunden sind.
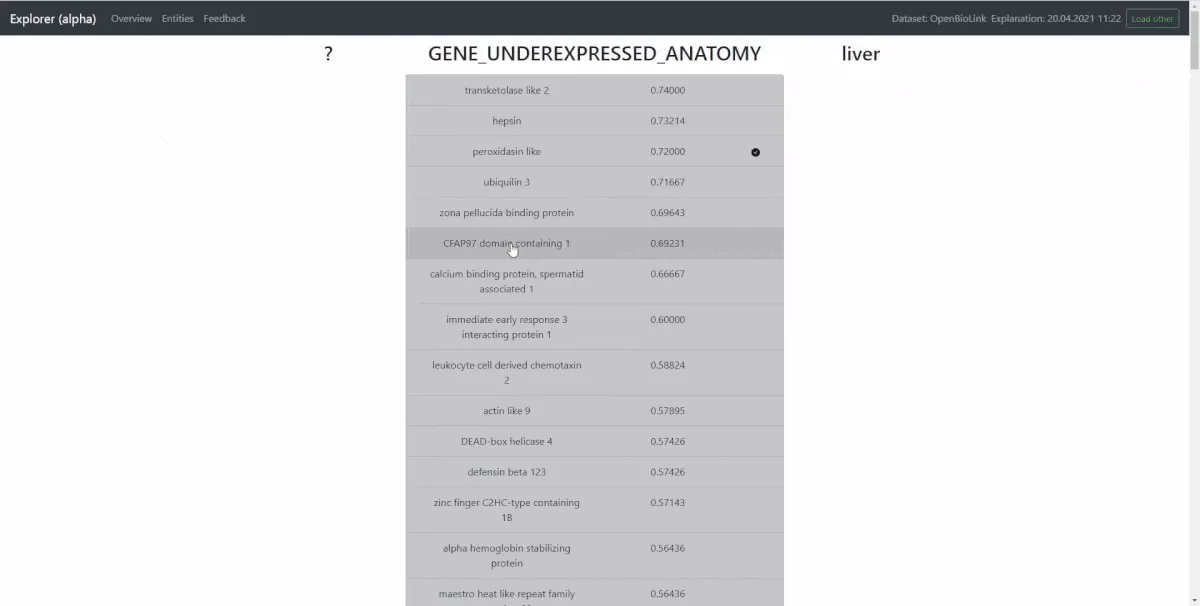
Hat der Benutzer einen Prediction Task ausgewählt bekommt er eine Liste mit allen vorhergesagten Entitäten und deren Konfidenzen. Entitäten die im Test-Set bekannt sind, werden mit einem “Checkmark” versehen. Dies bedeutet grundsätzlich nicht, dass Entitäten ohne “Checkmark” falsch sind, es bedeutet lediglich dass die Vorhersagen neu sind und deren Validität nicht automatisch überprüft werden kann. Wird eine Vorhersage ausgewählt, bekommt der Benutzer eine Übersicht über alle Regeln die zu der Vorhersage geführt haben. Besitzt eine Regel Variablen, können Instantierungen dieser Variablen eingesehen und somit die verwendeten Pfade überprüft werden. Alle Entitäten werden mit Links versehen, um schnell weiterführende Informationen über diese Entitäten zu erhalten.